假结结构
外观
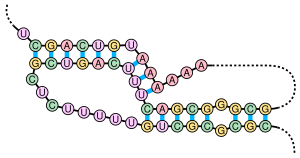

假结结构(pseudoknot)是一类RNA三级结构。假结结构包含至少两个茎环结构。其中,一个茎环结构的茎的一半插入了另一个茎环结构的茎结构中。假结结构最初于1982年在芜青花叶病毒中发现[2]。假结结构折叠成类似于绳结的三维结构,但却并不是真正的拓扑学的结。
预测与识别
[编辑]假结结构很难被计算生物学的检测手段查出,因为其对所在环境相当敏感,且具有“重叠的”本质。假结结构的碱基对的嵌入较差,即碱基对与其他的碱基对有一定重叠。这使得通过标准的动态规划方法对RNA序列中可能存在的假结结构的预测变得更加困难。动态规划通过一个递推记分系统来确认配对的茎结构,因而很难测出非嵌入的碱基对。更新的随机上下文无关文法也面临相同的问题。因此,像Mfold和Pfold这样的流行的二级结构预测方法并不能预测出目标序列中的假结结构。它们只能确认更稳定的假结结构中的两个茎。
可以通过动态规划的方法确认某些类型的假结结构,但这类方法不够详尽,而且在作为序列长度的函数时与进行与假结无关的算法时测量表现较差[3][4]。一个困扰许多预测最低的自由能的方法的问题是NP完全[5][6]。
生物学特征
[编辑]一些重要的生物学过程依赖于RNA分子形成的假结结构,这类RNA通常具有复杂三级结构。比如,RNA酶P的假结结构就是在进化过程中最保守的区域之一。端粒酶RNA的假结结构对其生物学活性亦至关重要[1],另外,几种病毒使用假结结构形成一个类似tRNA的结构模体,以侵入宿主细胞[7]。
参考文献
[编辑]- ^ 1.0 1.1 Chen JL, Greider CW. (2005). "Functional analysis of the pseudoknot structure in human telomerase RNA". Proc Natl Acad Sci USA 102(23): 8080–5.
- ^ Staple DW, Butcher SE. Pseudoknots: RNA structures with diverse functions. PLoS Biol. June 2005, 3 (6): e213 [2010-07-15]. PMC 1149493
 . PMID 15941360. doi:10.1371/journal.pbio.0030213. (原始内容存档于2019-09-15).
. PMID 15941360. doi:10.1371/journal.pbio.0030213. (原始内容存档于2019-09-15).
- ^ Rivas E, Eddy S. (1999). "A dynamic programming algorithm for RNA structure prediction including pseudoknots". J Mol Biol 285(5): 2053–2068.
- ^ Dirks, R.M. Pierce N.A. (2004) An algorithm for computing nucleic acid base-pairing probabilities including pseudoknots. "J Computation Chemistry". 25:1295-1304, 2004.
- ^ Lyngsø RB, Pedersen CN. (2000). "RNA pseudoknot prediction in energy-based models". J Comput Biol 7(3–4): 409–427.
- ^ Lyngsø, R. B. (2004). Complexity of pseudoknot prediction in simple models. Paper presented at the ICALP.
- ^ Pleij CW, Rietveld K, Bosch L. A new principle of RNA folding based on pseudoknotting.. Nucleic Acids Res. 1985, 13 (5): 1717–31. PMC 341107
 . PMID 4000943. doi:10.1093/nar/13.5.1717.
. PMID 4000943. doi:10.1093/nar/13.5.1717.
